新着情報
DNA言語に対する生成AI基盤モデルを開発
オーソログ進化パターンに基づく遺伝子配列再設計で異種生物での高発現を可能に
~バクテリアのプラスチック分解能力を最大約10倍向上~
北里大学未来工学部データサイエンス学科の榊原康文教授、慶應義塾大学および信州大学との共同研究グループは、系統進化の過程で保持・分化してきたオーソログ(共通祖先に由来する遺伝子)の配列パターンを学習し、導入先の生物(宿主)に適したDNA配列を生成する深層学習モデル「OrthologTransformer」を開発しました。45種の細菌を対象とした大規模ベンチマーク(450通りの種間変換)で、従来のコドン最適化を上回る性能を示し、プラスチック分解酵素PETaseを枯草菌(Bacillus subtilis)で発現させる実験では、反応生成物量が最大で約10倍向上しました。この研究成果は、2026年3月3日付で国際学術誌『Nature Communications』に掲載されました。
ポイント
・オーソログ(Ortholog)情報を学習する生成AI「OrthologTransformer」により、同義置換だけでなく非同義変異や挿入・欠失も自然な範囲で取り入れた遺伝子配列の再設計が可能。
・45種の細菌・450通りの種間変換で、宿主(ターゲット種)の天然オーソログに近い配列を生成し、従来のコドン最適化や既存手法を一貫して上回る性能を確認。
・PETase遺伝子を枯草菌で発現させる実験で、コドン最適化と比べて反応生成物量が最大約10倍に向上。
・ゲノム全体をデザインできるプラットフォームの構築に向けた生成AI基盤モデルを確立。
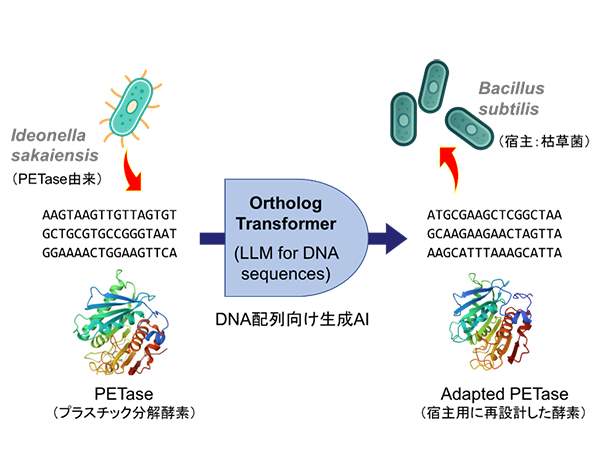
研究の概要
生成AI「OrthologTransformer」でDNA配列を再設計したプラスチック分解酵素を枯草菌に導入
生成AI「OrthologTransformer」でDNA配列を再設計したプラスチック分解酵素を枯草菌に導入
論文情報
【掲載誌】Nature Communications
【論文名】Cross-species gene redesign leveraging ortholog information and generative modeling
【著 者】Manato Akiyama, Motohiko Tashiro, Ying Huang, Mika Uehara, Taiki Kanzaki, Mitsuhiro Itaya, Masakazu Kataoka, Kenji Miyamoto, Yasubumi Sakakibara(責任著者)
【DOI】10.1038/s41467-026-69966-0
問い合わせ先
研究に関すること
北里大学 未来工学部
データサイエンス学科 人工知能研究室
教授 榊原 康文(さかきばら やすぶみ)
e-mail:sakakibara.yasubumi“AT”kitasato-u.ac.jp
データサイエンス学科 人工知能研究室
教授 榊原 康文(さかきばら やすぶみ)
e-mail:sakakibara.yasubumi“AT”kitasato-u.ac.jp
報道に関すること
学校法人北里研究所 広報室
〒108-8641 東京都港区白金5-9-1
TEL:03-5791-6422
e-mail:kohoh“AT”kitasato-u.ac.jp
〒108-8641 東京都港区白金5-9-1
TEL:03-5791-6422
e-mail:kohoh“AT”kitasato-u.ac.jp
※e-mailは上記アドレス“AT”の部分を@に変えてください。



